《自然·癌症》:中国科学家发现“癌王”对“合成致死”敏感的标志!
2022-11-16
这项研究发现了METTL16的一项全新功能,即METTL16会通过与DNA同源重组关键酶MRE11的相互作用来抑制DNA的同源重组修复。
作为最常见的RNA修饰之一,RNA腺嘌呤碱基在氮6位置的甲基化(简称m6A)自2011年重新进入科研人员视野以来,其研究热度一直不减[1]。而作为第二个被发现的RNA m6A甲基转移酶[2-3],METTL16最近也成为了生命科学的研究热点[4-5]。
近日,由美国妙佑医疗国际(Mayo Clinic)肿瘤科的楼振昆、上海同济大学医学院的袁健,以及华中科技大学同济医学院附属协和医院的陶凯雄领衔的研究团队,在《自然·癌症》杂志上发表关于METTL16功能的最新研究成果[6]。
奥拉帕利在同源重组缺陷型胰腺癌中已获美国FDA批准[7]。但是,仅有大约10%的胰腺癌患者带有同源重组缺陷型突变,大部分胰腺癌患者都无缘该疗法。因此,METTL16具有抑制DNA同源重组修复功能的这一发现,对PARP抑制剂在不带有同源重组缺陷型突变的胰腺癌患者中的使用具有重要意义。

Preview
来源: 生物谷
论文首页截图
接下来,就让我们来看看楼振昆、袁健,以及陶凯雄团队是如何展开这项研究的。
受启发于有关RNA m6A修饰在DNA修复功能方面的研究[8-9],研究人员决定探索m6A修饰酶(METTL3-METTL14,METTL16)在胰腺癌DNA损伤中扮演的角色。
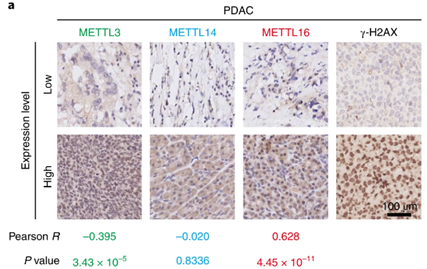
Preview
来源: 生物谷
这些结果说明,METTL16对DNA修复有抑制作用。
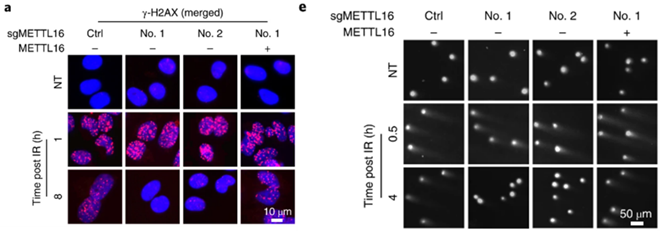
Preview
来源: 生物谷
敲除METTL16可以增强DNA修复,降低DSB水平
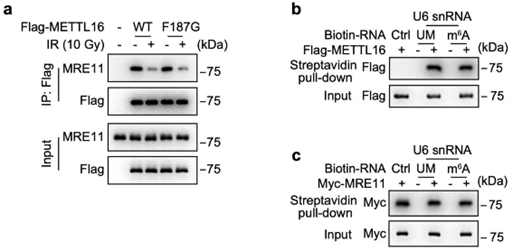
蛋白序列分析结果显示,METTL16存在着两个潜在的ATM/ATR(DNA修复相关激酶)磷酸化位点(Ser419和Ser455)。因此,研究人员猜测METTL16可能受ATM/ATR调控。结果确实如此。通过对这两个位点的磷酸化状态进行分析、构建位点突变模型等方法,研究者们发现ATM可以磷酸化METTL16上Ser419位点,而这会降低其对HDR的抑制作用。
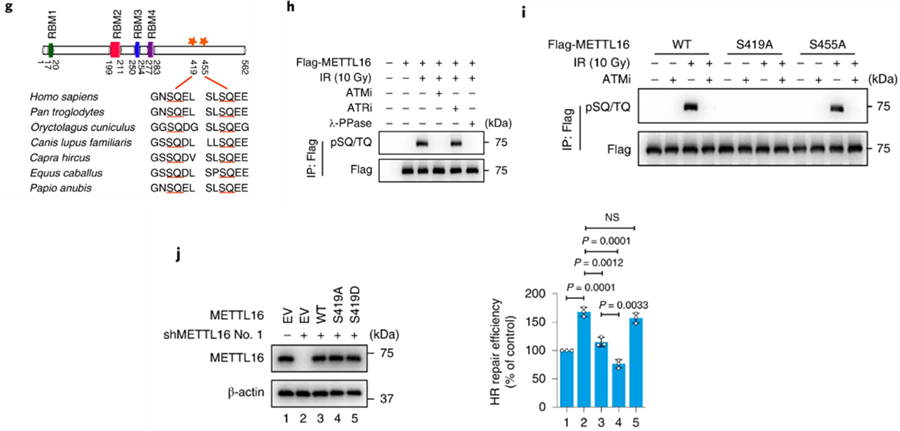
Preview
来源: 生物谷
ATM可以通过磷酸化METTL16来弱化其对HR修复的抑制作用
HDR修复DNA双链断裂主要有三大步骤,链末端切除(end resection)、3’-单链入侵同源模板链(strand invasion)、Holliday结的分解(resolution of Holliday Junction)。那么,METTL16会影响HDR的哪个步骤呢?
蛋白RPA32是一种单链DNA结合蛋白,与DNA复制过程中或DNA损伤情况下产生的3’单链结合,从而起到稳定单链的作用,而RPA32染色水平的增加则意味着细胞中3’-单链的增加。这提示到,METTL16会抑制链末端切除。
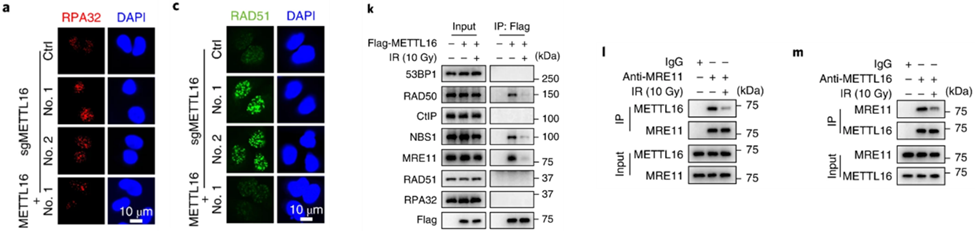
Preview
来源: 生物谷
METTL16通过与MRE11的相互作用来抑制HDR中的链末端切除步骤
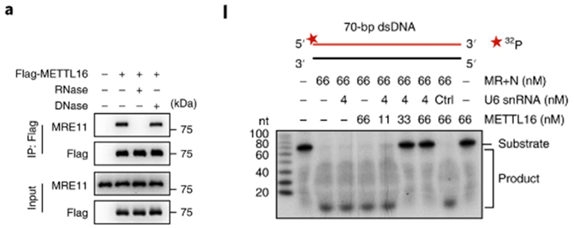
Preview
来源: 生物谷
METTL16通过RNA和MRE11产生相互作用并抑制后者的核酸酶活性
Preview
来源: 生物谷
考虑到METTL16对HDR的抑制作用,以及PARP抑制剂对HDR缺陷型肿瘤合成致死的特性,研究人员分析了PARP抑制剂奥拉帕利PARP抑制剂奥拉帕利对表达不同水平METTL16的BRCA1/2野生型胰腺癌BRCA1/2野生型胰腺癌细胞的杀伤效果。
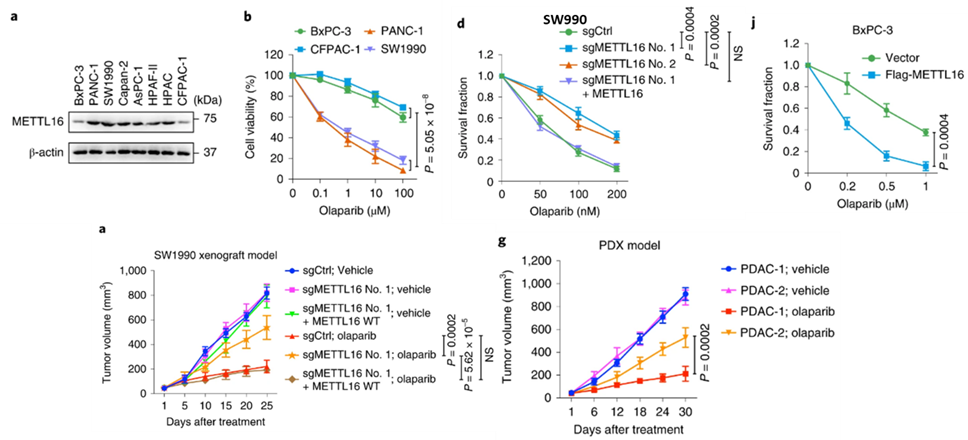
Preview
来源: 生物谷
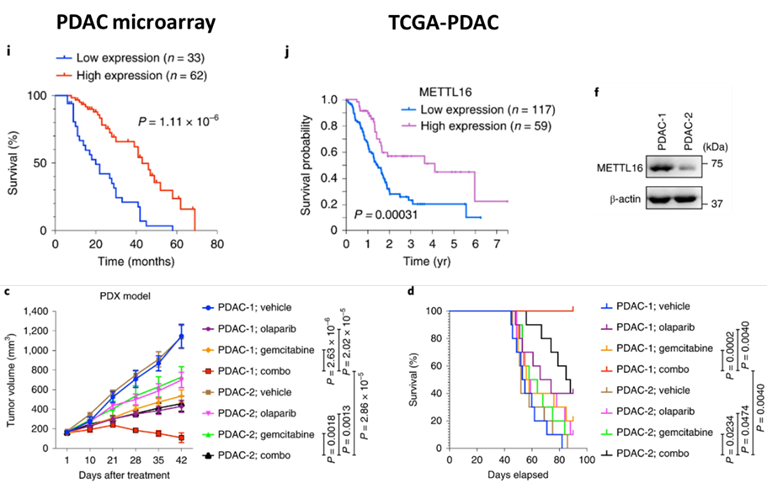
Preview
来源: 生物谷
同时,该研究揭示了METTL16的水平是一个潜在的胰腺癌预后指标,且吉西他滨+奥拉帕利的联合使用可能是治疗高表达METTL16胰腺癌的有效策略。
参考文献:
[1] Jiang X, Liu B, Nie Z, et al. The role of m6A modification in the biological functions and diseases. Signal Transduct Target Ther. 2021;6(1):74. Published 2021 Feb 21. doi:10.1038/s41392-020-00450-x
[2] Warda AS, Kretschmer J, Hackert P, et al. Human METTL16 is a N6-methyladenosine (m6A) methyltransferase that targets pre-mRNAs and various non-coding RNAs. EMBO Rep. 2017;18(11):2004-2014. doi:10.15252/embr.201744940
[3] Pendleton KE, Chen B, Liu K, et al. The U6 snRNA m6A Methyltransferase METTL16 Regulates SAM Synthetase Intron Retention. Cell. 2017;169(5):824-835.e14. doi:10.1016/j.cell.2017.05.003
[4] Su R, Dong L, Li Y, et al. METTL16 exerts an m6A-independent function to facilitate translation and tumorigenesis. Nat Cell Biol. 2022;24(2):205-216. doi:10.1038/s41556-021-00835-2
[5] Satterwhite ER, Mansfield KD. RNA methyltransferase METTL16: Targets and function. Wiley Interdiscip Rev RNA. 2022;13(2):e1681. doi:10.1002/wrna.1681
[6] Zeng X, Zhao F, Cui G, et al. METTL16 antagonizes MRE11-mediated DNA end resection and confers synthetic lethality to PARP inhibition in pancreatic ductal adenocarcinoma. Nat Cancer. 2022;3(9):1088-1104. doi:10.1038/s43018-022-00429-3
[7] Golan T, Hammel P, Reni M, et al. Maintenance Olaparib for Germline BRCA-Mutated Metastatic Pancreatic Cancer. N Engl J Med. 2019;381(4):317-327. doi:10.1056/NEJMoa1903387
[8] Zhang C, Chen L, Peng D, et al. METTL3 and N6-Methyladenosine Promote Homologous Recombination-Mediated Repair of DSBs by Modulating DNA-RNA Hybrid Accumulation. Mol Cell. 2020;79(3):425-442.e7. doi:10.1016/j.molcel.2020.06.017
[9] Yu F, Wei J, Cui X, et al. Post-translational modification of RNA m6A demethylase ALKBH5 regulates ROS-induced DNA damage response. Nucleic Acids Res. 2021;49(10):5779-5797. doi:10.1093/nar/gkab415
更多内容,请访问原始网站
文中所述内容并不反映新药情报库及其所属公司任何意见及观点,如有版权侵扰或错误之处,请及时联系我们,我们会在24小时内配合处理。
机构
-热门报告
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。


